Weltweit größtes Bakteriengenom sequenziert
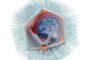
EM-Aufnahme des myzelbildenden Bodenbakteriums Ktedonobacter racemifer. Foto: Manfred Rohde, Helmholtz-Zentrum für Infektionsforschung GmbH<br>
Nur etwa ein Prozent des mikrobiellen Lebens um uns herum ist bisher im Labor kultiviert und beschrieben worden. Damit sind viele Potentiale der Mikroben noch unbekannt und nicht genutzt. Bestens untersucht waren lange Zeit nur Krankheitserreger wie multiresistente Staphylokokken oder biotechnologisch interessante E. coli-Stämme, die aber genetisch keineswegs repräsentativ sind.
Forscher des Leibniz-Instituts DSMZ–Deutsche Sammlung von Mikroorganismen und Zellkulturen GmbH aus Braunschweig und des Joint Genome Institute (JGI) in Kalifornien erarbeiten deshalb seit drei Jahren systematisch die sogenannte „Genomic Encyclopedia of Bacteria and Archaea“ (GEBA), die wesentlich breiter aufgestellt ist. Im Zuge dieser Forschungsarbeiten wurde nun das Genom des Bodenbakteriums Ktedonobacter racemifer entziffert, welches weltweit das bisher größte beschriebene Bakteriengenom ist. Die Ergebnisse der Forscher sind in der letzten Ausgabe der Standards in Genomic Sciences veröffentlicht.
„Im GEBA-Projekt untersuchen wir vor allem Mikroorganismen, die an „dunklen Flecken“ im Stammbaum der Bakterien stehen. Über die Auswertung von Genomdaten sind Rückschlüsse auf Verwandtschaftsverhältnisse zwischen Bakterien möglich“, erklärt PD Dr. Markus Göker, Bioinformatiker an der DSMZ. „Das Bakterium Ktedonobacter racemifer gehört zu den zehn, in Bezug auf ihre Stellung, wichtigsten Organismen im Bakterienstammbaum“.
„Das Genom des Gram-positiven Bodenbakteriums Ktedonobacter ist mit 11,453 Protein-codierenden Genen und 87 RNA-Genen das bisher größte dokumentierte Bakteriengenom“, erklärt Dr. Birte Abt, Wissenschaftlerin in der DSMZ-Abteilung Mikrobiologie. „Große Genome sind bei Bakterien mit einem komplizierten Lebenszyklus mit Myzel- und Sporenbildung nicht ungewöhnlich. Dieses enthält aber auch sehr viele Transposons oder auch Wiederholungssequenzen, sogenannte „springende Gene“. Diese kleinen DNA-Stücke können ihre Position im Genom verändern. Ihre Funktion ist aber noch nicht vollständig geklärt.“
„Der Bakterienstamm wurde 2006 von einem Forscherteam in Italien isoliert und in der DSMZ in der öffentlichen Sammlung hinterlegt. Daher konnte der Organismus hier vermehrt und qualitative hochwertige genomische DNA für die Sequenzierung aufbereitet werden“, berichtet Dr. Birte Abt weiter. „Für uns war es wichtig, diese sehr isoliert im Stammbaum stehende Bakteriengruppe zu sequenzieren, die bisher noch sehr wenige Organismen umfasst. Damit besteht immer eine Möglichkeit, neue interessante Proteinfamilien mit unbekannter Funktion zu entdecken“, so Markus Göker. „Vollständige Genomdaten sind auch aussagekräftiger für die Klassifikation von Mikroorganismen, als die bislang meist praktizierte evolutionäre Einordnung der Bakterien über kleine molekulare Markerstücke, wie vor allem die ribosomale 16S RNA.“
Neben wertvollen Einsichten in die Evolution bakterieller Genomgrößen einerseits und komplexer Lebenszyklen andererseits, hilft die Sequenzierung dieses Rekordgenoms auch dabei, die stammesverwandtschaftlichen Beziehungen von Mikroorganismen zu klären und damit ihre taxonomische Einteilung zu verbessern. Sowohl Ktedonobacter-Kulturen als auch annotierte Genomdaten stehen nun für weitergehende Forschungen frei zur Verfügung.
GEBA-Pilotprojekt
Das GEBA-Projekt (Genomic Encyclopedia of Bacteria and Archaea) hat zum Ziel, systematisch die Lücken bezüglich der Genomsequenzierung in den mikrobiellen Bereichen des Baums des Lebens zu füllen. Die DSMZ führt dieses Projekt in enger Kooperation mit dem JGI (Joint Genome Institute) in Kalifornien durch. Koordinator des GEBA-Pilotprojekts ist PD Dr. Hans-Peter Klenk, Leiter der Abteilung Mikroorganismen der DSMZ. Die Daten aus dem GEBA-Projekt sind im Portal „GenBank“ (www.ncbi.nlm.nih.gov/genbank/) hinterlegt und kostenfrei zugänglich unter img.jgi.doe.gov/cgi-bin/geba/main.cgi.
Originalpublikation:
Non-contiguous finished genome sequence and contextual data oft he filamentous soil bacterium Ktedonobacter racemifer type strain (SOSP1-21T). Standards in Genomic Sciences 5:97-111, 2011.
(veröffentlicht unter http://standardsingenomics.org/index.php/sigen)
Über die DSMZ
Das Leibniz-Institut DSMZ–Deutsche Sammlung von Mikroorganismen und Zellkulturen – ist eine Einrichtung der Leibniz-Gemeinschaft und mit seinen umfangreichen wissenschaftlichen Services und einem breiten Spektrum an Biomaterialien seit Jahrzehnten weltweiter Partner für Forschung und Industrie. Als einem der größten biologischen Ressourcenzentren seiner Art wurde der DSMZ die Übereinstimmung mit dem weltweit gültigen Qualitätsstandard ISO 9001:2008 bestätigt. Neben dem wissenschaftlichen Service bildet die sammlungsbezogene Forschung das zweite Standbein der DSMZ. Die Sammlung mit Sitz in Braunschweig existiert seit rund 40 Jahren und beherbergt mehr als 40.000 Kulturen. Die DSMZ ist die vielfältigste Sammlung weltweit: neben Pilzen, Hefen, Bakterien und Archaea werden dort auch menschliche und tierische Zellkulturen sowie Pflanzenviren und pflanzliche Zellkulturen erforscht und archiviert.
Media Contact
Alle Nachrichten aus der Kategorie: Biowissenschaften Chemie
Der innovations-report bietet im Bereich der "Life Sciences" Berichte und Artikel über Anwendungen und wissenschaftliche Erkenntnisse der modernen Biologie, der Chemie und der Humanmedizin.
Unter anderem finden Sie Wissenswertes aus den Teilbereichen: Bakteriologie, Biochemie, Bionik, Bioinformatik, Biophysik, Biotechnologie, Genetik, Geobotanik, Humanbiologie, Meeresbiologie, Mikrobiologie, Molekularbiologie, Zellbiologie, Zoologie, Bioanorganische Chemie, Mikrochemie und Umweltchemie.
Neueste Beiträge

Diamantstaub leuchtet hell in Magnetresonanztomographie
Mögliche Alternative zum weit verbreiteten Kontrastmittel Gadolinium. Eine unerwartete Entdeckung machte eine Wissenschaftlerin des Max-Planck-Instituts für Intelligente Systeme in Stuttgart: Nanometerkleine Diamantpartikel, die eigentlich für einen ganz anderen Zweck bestimmt…
Neue Spule für 7-Tesla MRT | Kopf und Hals gleichzeitig darstellen
Die Magnetresonanztomographie (MRT) ermöglicht detaillierte Einblicke in den Körper. Vor allem die Ultrahochfeld-Bildgebung mit Magnetfeldstärken von 7 Tesla und höher macht feinste anatomische Strukturen und funktionelle Prozesse sichtbar. Doch alleine…

Hybrid-Energiespeichersystem für moderne Energienetze
Projekt HyFlow: Leistungsfähiges, nachhaltiges und kostengünstiges Hybrid-Energiespeichersystem für moderne Energienetze. In drei Jahren Forschungsarbeit hat das Konsortium des EU-Projekts HyFlow ein extrem leistungsfähiges, nachhaltiges und kostengünstiges Hybrid-Energiespeichersystem entwickelt, das einen…