Proteinaggregation: Zusammenlagerung von Proteinen nicht nur bei Alzheimer und Parkinson relevant

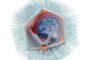
Querschnitt des 3D-Modells einer Amyloidfibrille vor dem Hintergrund einer Kryoelektronenmikroskopie-Aufnahme. Gelb hervorgehoben ist eine PI3K-SH3-Domäne. FZJ / Christine Röder
Bei neurodegenerativen Erkrankungen spielen Amyloid-Fibrillen eine gefährliche Rolle. Wissenschaftlerinnen und Wissenschaftler der Heinrich-Heine-Universität Düsseldorf (HHU) und des Forschungszentrums Jülich konnten nun mit Hilfe der Kryoelektronenmikroskopie (Kryo-EM) erstmals die räumliche Struktur der Fibrillen entschlüsseln, die sich aus PI3K-SH3-Domänen bilden – ein für die Forschung wichtiges Modellsystem. Die untersuchten Fibrillen stehen zwar selbst nicht mit einer Erkrankung in Verbindung, aber die erzielten Ergebnisse und entwickelten Methoden können zum Verstehen von Krankheiten wie Alzheimer und Parkinson dienen.
Proteine sind zentrale Bausteine von lebender Materie. Diese aus einzelnen Aminosäuren zusammengesetzten komplexen Moleküle bestehen teilweise aus tausenden einzelner Atome und sind dreidimensional geformt; man spricht von Faltungen. Von der Faltung hängt die biologische Funktion ab.
Kommt es zu fehlerhaften Faltungen, werden die Proteine nicht nur nutzlos, sie können sogar toxisch wirken. Man geht heute davon aus, dass viele neurodegenerative Erkrankungen durch fehlgefaltete Proteine ausgelöst werden.
Sie bilden Ablagerungen an kritischen Stellen des Nervengewebes. Es bilden sich zunächst faserartige Strukturen, die sogenannten Amyloidfibrillen. Mehrerer dieser können sich zu den typischen Plaques verknäulen, die im Gehirngewebe nachweisbar sind und die Nervenzellen beeinträchtigen, schädigen oder töten können.
Die PI3K-SH3-Domänen sind Teil eines größeren Proteins, sie können aber auch allein in gefaltete Form gebracht werden. Sie spielen in der zellulären Kommunikation eine wichtige Rolle. Diese Domänen werden seit vielen Jahren als Modellsysteme genutzt, um die Proteinfaltung zu untersuchen und dabei auch die Ursachen von Fehlfaltungen zu ermitteln.
Denn man hat entdeckt, dass auch diese Domänen Amyloidfibrillen bilden können, die sich von den für Erkrankungen typischen Fibrillen nicht unterscheiden und sogar genauso giftig für Zellen sind. Tatsächlich können potenziell sogar alle Proteine Fibrillen bilden; der gesunde Körper muss sich dieses Prozesses ständig aktiv erwehren.
Viele grundlegende Entdeckungen von Amyloidfibrillen, die direkt auf krankheitsrelevante Proteine übertragen werden können, wurden an diesem Modellsystem gemacht. „Was aber bisher nicht bekannt war, ist die genaue dreidimensionale Struktur der Fibrillen aus den PI3K-SH3-Domänen“, so Prof. Dr. Gunnar Schröder, Professor für rechnergestützte Strukturbiologie an der HHU und gleichzeitig Arbeitsgruppenleiter am Forschungszentrum Jülich.
„Diese Strukturen konnten wir nun mithilfe der Kryo-EM aufklären“, ergänzt Prof. Dr. Alexander Büll, der zusammen mit Schröder Corresponding Author der bei Nature Communications veröffentlichten Studie ist. Büll war bis Anfang 2019 Juniorprofessor an der HHU und ist nun Professor am Department of Biotechnology and Biomedicine an der Technischen Universität von Dänemark in Lyngby. Prof. Schröder ergänzt zur Bedeutung dieser Strukturaufklärung: „Jetzt, wo wir die räumliche Struktur kennen, können viele der früheren Daten neu oder besser interpretiert werden.“
„Die Kryoelektronenmikroskopie ist ein hervorragendes Werkzeug, um die dreidimensionale Struktur der Fibrillen aufzuklären“, betont Christine Röder, Erstautorin der Studie und Doktorandin in der Arbeitsgruppe von Prof. Schröder in Jülich. Bei dieser Methode, für deren Entwicklung 2017 der Nobelpreis für Chemie vergeben wurde, können komplexe Biomoleküle, die nur in wässriger Umgebung ihre natürliche Form haben, mit atomarer Auflösung dargestellt werden.
Dazu werden die in Wasser gelösten Proben – zum Beispiel Proteine – in kürzester Zeit bei sehr tiefen Temperaturen eingefroren und damit in ihrer natürlichen Struktur fixiert. So ist es möglich, sie in diesem Zustand elektronenmikroskopisch zu untersuchen. Dies gelingt allerdings nicht mit einem „Schuss“, sondern nur durch eine Folge vieler Aufnahmen, die das Protein aus unterschiedlichen Winkeln zeigen. Anschließend setzen Computer die vielen Einzelaufnahmen zu einem dreidimensionalen Bild zusammen.
Christine Röder, Nicola Vettore, Lena N. Mangels, Lothar Gremer, Raimond B. G. Ravelli, Dieter Willbold, Wolfgang Hoyer, Alexander K. Buell & Gunnar F. Schröder, Atomic structure of PI3-kinase SH3 amyloid fibrils by cryo-electron microscopy, Nature Communications (2019) 10:3754
DOI: 10.1038/s41467-019-11320-8
Media Contact
Weitere Informationen:
http://www.hhu.de/Alle Nachrichten aus der Kategorie: Biowissenschaften Chemie
Der innovations-report bietet im Bereich der "Life Sciences" Berichte und Artikel über Anwendungen und wissenschaftliche Erkenntnisse der modernen Biologie, der Chemie und der Humanmedizin.
Unter anderem finden Sie Wissenswertes aus den Teilbereichen: Bakteriologie, Biochemie, Bionik, Bioinformatik, Biophysik, Biotechnologie, Genetik, Geobotanik, Humanbiologie, Meeresbiologie, Mikrobiologie, Molekularbiologie, Zellbiologie, Zoologie, Bioanorganische Chemie, Mikrochemie und Umweltchemie.
Neueste Beiträge

Diamantstaub leuchtet hell in Magnetresonanztomographie
Mögliche Alternative zum weit verbreiteten Kontrastmittel Gadolinium. Eine unerwartete Entdeckung machte eine Wissenschaftlerin des Max-Planck-Instituts für Intelligente Systeme in Stuttgart: Nanometerkleine Diamantpartikel, die eigentlich für einen ganz anderen Zweck bestimmt…
Neue Spule für 7-Tesla MRT | Kopf und Hals gleichzeitig darstellen
Die Magnetresonanztomographie (MRT) ermöglicht detaillierte Einblicke in den Körper. Vor allem die Ultrahochfeld-Bildgebung mit Magnetfeldstärken von 7 Tesla und höher macht feinste anatomische Strukturen und funktionelle Prozesse sichtbar. Doch alleine…

Hybrid-Energiespeichersystem für moderne Energienetze
Projekt HyFlow: Leistungsfähiges, nachhaltiges und kostengünstiges Hybrid-Energiespeichersystem für moderne Energienetze. In drei Jahren Forschungsarbeit hat das Konsortium des EU-Projekts HyFlow ein extrem leistungsfähiges, nachhaltiges und kostengünstiges Hybrid-Energiespeichersystem entwickelt, das einen…