KI zur Vorhersage von Proteinstruktur entwickelt
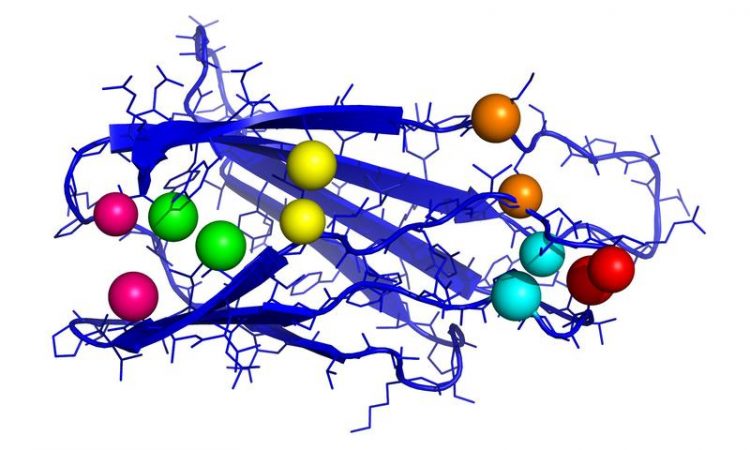
Fibronektin spielt bei der Wundheilung eine bedeutende Rolle. Die Grafik zeigt einen wichtigen Teil des Proteins mit Kontaktpaaren (jeweils gleichfarbige Kugeln). Abbildung: Ines Reinartz, KIT
Proteine können mit anderen Molekülen durch Eindringen oder Umschließen interagieren, je nach Form. Diese lässt sich – anders als beim Blick in den heimischen Werkzeugkasten – nicht ohne weiteres feststellen, sondern nur mit teuren und aufwendigen Experimenten.
Forscherinnen und Forscher des Steinbuch Centre for Computing (SCC), dem Rechenzentrum des KIT, haben dafür zunächst Datenbanken für Proteinsequenzen durchkämmt und gleiche Proteine unterschiedlicher Spezies verglichen. „Hämoglobin, das in unserem Körper für den Sauerstofftransport zuständig ist, gibt es auch beim Insekt, bei der Feldmaus und beim Schimpansen“, erklärt Markus Götz, Datenanalyst beim SCC.
Den Aufbau eines Proteins kann man sich dabei wie eine Perlenkette vorstellen, an der Proteinteile, die Aminosäuren, aufgereiht sind. Seine dreidimensionale Struktur – und damit seine Eigenschaften – erhält es, indem sich manche weit voneinander entfernte „Perlen“ zu Paaren zusammenschließen und das Protein so falten.
Bei verschiedenen Organismen können sich diese Paarungen unterscheiden, die Eigenschaften des Proteins bleiben aber dennoch gleich. „Schädliche Mutationen wurden im Laufe der Evolution ausgefiltert“, sagt Götz.
Das Team um Götz hat nun einer Künstlichen Intelligenz (KI) beigebracht, welche Kopplungen in bekannten Proteinsequenzen evolutionär erfolgreich waren. „Wir erwarten, dass das System so auch Rückschlüsse auf den Aufbau unbekannter Proteinsequenzen ziehen kann“, so Götz.
Der Nutzen: „Es ist sehr einfach zu bestimmen, aus welchen Aminosäuren eine Proteinkette besteht. Proteinstrukturen direkt experimentell zu bestimmen, ist aber sehr aufwendig und kostet Millionen“, ergänzt Alexander Schug vom SCC.
Der Ansatz, Kontakte in Proteinen von einer KI vorhersagen zu lassen, ist nicht ganz neu. „Aktuell werden dafür vor allem Methoden aus der Bildverarbeitung eingesetzt“, sagt Götz. Solche Neuronalen Netzwerke könnten Muster gut erkennen. Bei der Proteinstruktur spielten aber besonders jene Kontakte von Proteinteilen eine Rolle, die besonders weit auseinander liegen, weil sie beim Falten einen stärkeren Einfluss auf die Form haben als solche, die nahe beieinander liegen.
„Daher verfolgen wir stattdessen einen Ansatz aus der automatisierten Sprachübersetzung. Wir betrachten die Aminosäureketten als Sätze, die in eine andere Sprache übersetzt werden.“ Sogenannte „Self-Attention Neural Networks“ kommen in populären Übersetzungsprogrammen zum Einsatz. Sie können erkennen, welche Teile des Satzes miteinander in Beziehung stehen oder – im Proteinkontext – welche Aminosäuren miteinander einen Kontakt bilden.
Details zum KIT-Zentrum Information · Systeme · Technologien (in englischer Sprache): http://www.kcist.kit.edu
Weitere Materialien:
Das Video zeigt, wie sich das „Zellkleber“-Protein Fibronektin aus dem funktionalen Zustand entfaltet und dann wieder faltet (Animation: Ines Reinartz, KIT):
https://www.kit.edu/downloads/proteinfaltung.mp4
Weiterer Kontakt:
Dr. Felix Mescoli, Redakteur/Pressereferent, Tel.: +49 721 608 48120, E-Mail: felix.mescoli@kit.edu
Als „Die Forschungsuniversität in der Helmholtz-Gemeinschaft“ schafft und vermittelt das KIT Wissen für Gesellschaft und Umwelt. Ziel ist es, zu den globalen Herausforderungen maßgebliche Beiträge in den Feldern Energie, Mobilität und Information zu leisten. Dazu arbeiten rund 9 300 Mitarbeiterinnen und Mitarbeiter auf einer breiten disziplinären Basis in Natur-, Ingenieur-, Wirtschafts- sowie Geistes- und Sozialwissenschaften zusammen. Seine 25 100 Studierenden bereitet das KIT durch ein forschungsorientiertes universitäres Studium auf verantwortungsvolle Aufgaben in Gesellschaft, Wirtschaft und Wissenschaft vor. Die Innovationstätigkeit am KIT schlägt die Brücke zwischen Erkenntnis und Anwendung zum gesellschaftlichen Nutzen, wirtschaftlichen Wohlstand und Erhalt unserer natürlichen Lebensgrundlagen.
Diese Presseinformation ist im Internet abrufbar unter: http://www.sek.kit.edu/presse.php
Dr. Felix Mescoli, Redakteur/Pressereferent, Tel.: +49 721 608 48120, E-Mail: felix.mescoli@kit.edu
http://www.kcist.kit.edu
https://www.kit.edu/downloads/proteinfaltung.mp4
http://www.sek.kit.edu/presse.php
Media Contact
Alle Nachrichten aus der Kategorie: Biowissenschaften Chemie
Der innovations-report bietet im Bereich der "Life Sciences" Berichte und Artikel über Anwendungen und wissenschaftliche Erkenntnisse der modernen Biologie, der Chemie und der Humanmedizin.
Unter anderem finden Sie Wissenswertes aus den Teilbereichen: Bakteriologie, Biochemie, Bionik, Bioinformatik, Biophysik, Biotechnologie, Genetik, Geobotanik, Humanbiologie, Meeresbiologie, Mikrobiologie, Molekularbiologie, Zellbiologie, Zoologie, Bioanorganische Chemie, Mikrochemie und Umweltchemie.
Neueste Beiträge

Bakterien für klimaneutrale Chemikalien der Zukunft
Forschende an der ETH Zürich haben Bakterien im Labor so herangezüchtet, dass sie Methanol effizient verwerten können. Jetzt lässt sich der Stoffwechsel dieser Bakterien anzapfen, um wertvolle Produkte herzustellen, die…

Batterien: Heute die Materialien von morgen modellieren
Welche Faktoren bestimmen, wie schnell sich eine Batterie laden lässt? Dieser und weiteren Fragen gehen Forschende am Karlsruher Institut für Technologie (KIT) mit computergestützten Simulationen nach. Mikrostrukturmodelle tragen dazu bei,…

Porosität von Sedimentgestein mit Neutronen untersucht
Forschung am FRM II zu geologischen Lagerstätten. Dauerhafte unterirdische Lagerung von CO2 Poren so klein wie Bakterien Porenmessung mit Neutronen auf den Nanometer genau Ob Sedimentgesteine fossile Kohlenwasserstoffe speichern können…