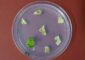
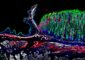
Intelligente Software zum besseren Verständnis der Entwicklung von Pflanzengewebe

Die Mikroskopie liefert Bilder für den Algorithmus, der dann die zellulären Strukturen von Pflanzen abgrenzt und die Segmentierung klarer macht.
K. Schneitz / TUM
Frei für die Berichterstattung über die TU München.
Unter Einsatz von Künstlicher Intelligenz haben Forscherinnen und Forscher ein neuartiges computergestütztes Verfahren der Bildverarbeitung für die Pflanzenwissenschaften entwickelt. In bisher nicht gekannter Präzision ermöglicht es die detailgetreue 3D-Darstellung aller Zellen in verschiedensten pflanzlichen Organen.
Pflanzenorgane wie die Wurzel, die Sprossachse, die Blätter und die Blüten haben mannigfaltige Aufgaben. Sie sorgen dafür, dass die Pflanze sich entwickeln kann und wächst und dass sie durch Bildung von Samen den Fortbestand ihrer Art sichern kann. Doch wie formen Pflanzen ihre Organe? Wie wird die genetische Information genutzt, um die dreidimensionale Form – die Gestalt – eines Organismus aufzubauen?
Kay Schneitz, Professor für Entwicklungsbiologie der Pflanzen an der Technischen Universität München (TUM), befasst sich mit den molekularen Grundlagen der Blütenentwicklung und der pflanzlichen Reproduktion. Er ist Ko-Sprecher einer Forschungsgruppe der Deutschen Forschungsgemeinschaft (DFG-FOR 2581), die untersucht, wie Zellen ihr Verhalten koordinieren, um der Pflanze eine Gestalt zu geben (Morphogenese).
Detaillierte 3D-Analyse des Aufbaus von Pflanzengewebe mittels Software
In der Vergangenheit wurden mehrheitlich 2D-Techniken verwendet, um zu analysieren, wie eine Pflanze ihre Gestalt erhält. „Morphogenese findet aber natürlich im dreidimensionalen Raum sowie in der vierten Dimension, der Zeit, statt“, sagt Prof. Schneitz. „2D-Ansätze, zum Beispiel mittels Gewebeschnitten, erlauben daher nur partielle Einblicke in diesen Prozess und liefern leider oft auch falsche Ergebnisse.“
Prof. Schneitz und seine Mitarbeiter, die Molekularbiologen Athul Vijayan und Rachele Tofanelli, haben nun gemeinsam mit Kolleginnen und Kollegen aus den Computerwissenschaften und der Physik ein neues Werkzeug entwickelt, das dieses Problem behebt.
Vom Computercode bis hin zu einer benutzerfreundlichen grafischen Schnittstelle steht Forschenden auf der ganzen Welt nun eine Open Source Software namens PlantSeg zur Verfügung, die die bisher genaueste und vielseitigste Analyse der Entwicklung von Pflanzengewebe in 3D möglich macht.
Maschinelles Lernen – die Software wird trainiert
Wenn Forscher die Morphogenese von Geweben auf zellulärer Ebene untersuchen wollen, ist es notwendig, einzelne Zellen abzubilden. Dazu müssen die Zellen voneinander getrennt oder „segmentiert“ werden, um die Veränderungen im Laufe der Zeit zu analysieren.
„In Pflanzen hat man oft Zellen, die extrem regelmäßig aussehen. Sie erscheinen im Querschnitt wie Rechtecke oder Zylinder“, sagt Anna Kreshuk, Senior-Autorin einer kürzlich erschienenen Publikation über die Forschungsarbeit der Gruppe. „Aber man hat auch Zellen mit Einbuchtungen und Vorsprüngen, die eher wie Puzzleteile aussehen. Diese sind wegen ihrer Unregelmäßigkeit schwieriger zu segmentieren.“
Hierzu setzte das Team maschinelles Lernen, eine Methode aus dem Bereich Künstlicher Intelligenz, ein. Die Wissenschaftlerinnen und Wissenschaftler trainierten PlantSeg an 3D-Mikroskopbildern reproduktiver Organe und Wurzeln des Pflanzenmodells Arabidopsis thaliana, auch als Ackerschmalwand bekannt. Dabei musste der Algorithmus lernen, die Inkonsistenzen der Zellen in Größe und Form zu interpretieren. Diese Herausforderung meisterten sie so gut, dass die Software jetzt bei praktisch allen pflanzlichen Organen eingesetzt werden kann.
PlantSeg – ein breites Anwendungsspektrum
PlantSeg ermöglicht nicht nur Untersuchungen zur Entwicklung von pflanzlichen Organen in bisher nicht gekannter Präzision, sondern auch die Analyse von Gewebeveränderungen die durch Schädlingsbefall oder Umweltstresse wie Hitze entstehen. Dadurch erhoffen sich die Wissenschaftlerinnen und Wissenschaftler ein besseres Verständnis davon, wie Pflanzen auf Umweltbedingungen reagieren.
Die Methode könnte man auch für tierisches Gewebe adaptieren. „Bei Tieren müssten wir wahrscheinlich Teile der Software neu trainieren, aber es würde funktionieren“, erklärt Kreshuk. Die Forschungsgruppe hätte dann ein Werkzeug geschaffen, dass über die Pflanzenwelt hinaus von Bedeutung wäre und mit dem zum Beispiel auch krankheitsbedinge Gewebeveränderungen viel genauer analysiert werden könnten.
Mehr Informationen:
Der Forschungsgruppe gehörten Experten des EMBL, der Universität Heidelberg, der TUM, der University of Warwick und des Max-Planck-Instituts für Züchtungsforschung in Köln an.
Wissenschaftliche Ansprechpartner:
Prof. Dr. Kay Schneitz
Technische Universität München
Professur für Entwicklungsbiologie der Pflanzen
Tel.: +49 (8161) 71 – 5438
kay.schneitz(at)tum.de
https://www.professoren.tum.de/schneitz-kay-heinrich
https://www.plantdev.wzw.tum.de/home.html
Originalpublikation:
Adrian Wolny et al.: Accurate and versatile 3D segmentation of plant tissues at cellular resolution. eLifeScience, online veröffentlicht am 29. Juli 2020: https://elifesciences.org/articles/57613
Weitere Informationen:
https://www.plantmorphodynamics.com (DFG Forschungsgrupe)
https://www.tum.de/nc/die-tum/aktuelles/pressemitteilungen/details/36237/ (Pressemitteilung)
https://mediatum.ub.tum.de/1575701 (hochauflösendes Bildmaterial)
https://youtu.be/PNN_lzi8wGg (Video)
https://github.com/hci-unihd/plant-seg (Softwaredownload)
Media Contact
Alle Nachrichten aus der Kategorie: Biowissenschaften Chemie
Der innovations-report bietet im Bereich der "Life Sciences" Berichte und Artikel über Anwendungen und wissenschaftliche Erkenntnisse der modernen Biologie, der Chemie und der Humanmedizin.
Unter anderem finden Sie Wissenswertes aus den Teilbereichen: Bakteriologie, Biochemie, Bionik, Bioinformatik, Biophysik, Biotechnologie, Genetik, Geobotanik, Humanbiologie, Meeresbiologie, Mikrobiologie, Molekularbiologie, Zellbiologie, Zoologie, Bioanorganische Chemie, Mikrochemie und Umweltchemie.
Neueste Beiträge

Neue Industrie-4.0-Lösung für niedrigschwelligen Zugang zu Datenräumen
»Energizing a Sustainable Industry« – das Motto der Hannover Messe 2024 zeigt klar, wie wichtig eine gleichermaßen leistungsstarke und nachhaltige Industrie für den Fertigungsstandort Deutschland ist. Auf der Weltleitmesse der…

Quantenpräzision: Eine neue Art von Widerstand
Physikforschende der Universität Würzburg haben eine Methode entwickelt, die die Leistung von Quantenwiderstands-Normalen verbessern kann. Sie basiert auf einem Quantenphänomen namens anomaler Quanten-Hall-Effekt. In der industriellen Produktion oder in der…

Sicherheitslücke in Browser-Schnittstelle erlaubt Rechnerzugriff über Grafikkarte
Forschende der TU Graz waren über die Browser-Schnittstelle WebGPU mit drei verschiedenen Seitenkanal-Angriffen auf Grafikkarten erfolgreich. Die Angriffe gingen schnell genug, um bei normalem Surfverhalten zu gelingen. Moderne Websites stellen…