Kein Schlupfloch für das HI-Virus

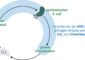
Schematische Darstellung des Proteins gp120, mit dem sich das HI-Virus Zugang zur Wirtszelle verschafft. Bild: Max-Planck-Institut für Informatik
Das Prinzip von Schlüssel und Schloss ist in der Natur weit verbreitet: Zellen nutzen es beispielsweise, um verschiedenste Substanzen zu transportieren oder um Erbinformationen korrekt zu kopieren. Aber auch lebensbedrohliche Viren wie das HI-Virus verschaffen sich über die molekularen Schließmechanismen Zugang zu den Wirtszellen. Wissenschaftler am Max-Planck-Institut für Informatik in Saarbrücken tragen zusammen mit Wissenschaftlern des British Columbia Centre for Excellence in HIV/AIDS im kanadischen Vancouver nun dazu bei, das zu verhindern: Sie können für jede Virus-Variante Details des Schließsystems herausfinden. Dazu entwickelten sie eine bioinformatische Methode, die den Schlüssel des HI-Virus zur Wirtszelle räumlich darstellt und ihn physikalisch und chemisch charakterisiert. Diese Methode, Strukturdeskriptor genannt, macht es leichter vorherzusagen, wie neuartige HIV-Medikamente bei einem bestimmten Patienten wirken und ob sie gesundheitliche Risiken für den Patienten bergen. Darüber hinaus kann der Strukturdeskriptor helfen, die Mechanismen der Infektion und des Krankheitsverlaufs besser zu verstehen (PLoS Computational Biology, März 2007).
HIV-Medikamente zielen in der Regel auf wichtige Prozesse im Vermehrungszyklus des Virus ab: gängige Wirkstoffe hindern das Virus beispielsweise daran, sein Genom von der RNA-Form nach DNA zurückzuübersetzen, so dass dieses nicht in das Erbgut der Wirtszelle eingebaut werden kann. In naher Zukunft kommt ein neuer Medikamenten-Typus auf den Markt, die sogenannten Korezeptor-Inhibitoren. Diese verwehren den HI-Viren den Zutritt zu den Zellen, indem sie ein bestimmtes Türschloss auf deren Oberfläche blockieren. Wie sie wirken, hängt davon ab, welchen molekularen Schlüssel die Viren besitzen. Das herauszufinden, ist mit dem von den Max-Planck-Wissenschaftlern entwickelten Strukturdeskriptor vergleichsweise einfach und zuverlässig möglich.
Die Forscher charakterisieren mit ihrer Methode die V3-Loop, die schleifenförmige Spitze des viralen Oberflächenproteins gp120 – des molekularen Schlüssels auf der Virusoberfläche. Je nachdem, wie die V3-Loop geformt ist, kann er an einen der beiden Korezeptoren an der Wand der Wirtszelle, CCR5 oder CXCR4, binden. Dabei müssen die Strukturen von V3-Loop und Korezeptor räumlich und chemisch so präzise ineinander greifen wie ein Schlüssel und das zugehörige Schloss. „Momentan werden mehrere Korezeptor-Inhibitoren in klinischen Studien getestet, das erste derartige Medikament kommt voraussichtlich noch dieses Jahr auf den Markt“, erklärt Oliver Sander vom Max-Planck-Institut für Informatik. Bestechend an dem Konzept der neuen Medikamente ist, dass es an einem Punkt angreift, der nicht vom Virus, sondern von der Wirtszelle abhängt. Einem Korezeptor-Inhibitor können die schnellen Mutationen des Virus daher keinen Strich durch die Rechnung machen.
Bevor der richtige Korezeptor-Inhibitor allerdings dem Patienten verabreicht werden kann, muss bekannt sein, welche der beiden Andockstellen CCR5 oder CXCR4 das Virus gerade verwendet. „Dazu musste man bisher in einer Blutprobe des Patienten untersuchen, an welchen Korezeptor seine Viren tatsächlich andocken. Das dauert viele Tage bis Wochen und kostet sehr viel Geld“, erläutert Sander. „Viel schneller geht es, aus der Blutprobe nur die DNA-Sequenz des Virus zu ermitteln und daraus computergestützt die Struktur des V3-Loops zu errechnen.“ Mit der am Max-Planck-Institut für Informatik entwickelten bioinformatischen Methode rückt das in greifbare Nähe: „Die Methode funktioniert in zwei Stufen“, erklärt Sander, „zunächst einmal verknüpft man in einer Datenbank konkrete virale Varianten mit der dazugehörigen Information über den Korezeptor und die Struktur des V3-Loop.“ Diese Datensätze sind im Internet bereits als „geno2pheno[coreceptor]“ abrufbar. Sie erlauben aber nur eine grobe Schätzung, wenn eine bestimmte DNA-Sequenz in der Datenbank noch nicht erfasst ist. Daher kommt in der zweiten Stufe ein statistisches Lernverfahren dazu, welches mit Hilfe des Strukturdeskriptors vorhersagt, welcher Rezeptor verwendet wird. „Neu daran ist, dass mit dem Strukturdeskriptor erstmalig dreidimensionale Informationen zur Bestimmung des Korezeptors hinzugezogen werden. Unsere Ergebnisse zeigen, dass das die Vorhersagen sehr viel genauer macht“, sagt Sander.
Für eine Therapie mit Korezeptor-Inhibitoren reicht es allerdings nicht aus, nur einmal festzustellen, welche Andockstelle das Virus verwendet. Meist geschieht der Eintritt in die Wirtszelle zu Beginn der Infektion am Korezeptor CCR5, im späteren Krankheitsverlauf wechselt das Virus auf den Korezeptor CXCR4. Welcher der beiden Korezeptoren verwendet wird, muss deshalb auch im Verlauf der Therapie immer wieder kontrolliert werden.
Anhand des Strukturdeskriptors und der Datensätze können Virologen nun erforschen, warum welche Virusvariante gerade einen bestimmten Korezeptor verwendet. Möglicherweise markiert der Wechsel des Korezeptors einen kritischen Punkt im Verlauf der Krankheit. „Deswegen ist es wichtig, ständig zu überwachen, welcher Korezeptor gerade verwendet wird. Im schlimmsten Fall könnte es sein, dass man die Infektion durch die Blockade des falschen Korezeptors sogar vorantreibt.“ In Zukunft könnte Sanders Strukturdeskriptor dabei helfen, diese und ähnliche Fragen zu klären.
Originalveröffentlichung:
Oliver Sander, Tobias Sing, Ingolf Sommer, Andrew J. Low, Peter K. Cheung, P. Richard Harrigan, Thomas Lengauer und Francisco S. Domingues
Structural Descriptors of gp120 V3 Loop for the Prediction of HIV-1 Coreceptor Usage; PLoS Computational Biology, März 2007
Media Contact
Weitere Informationen:
http://www.mpg.deAlle Nachrichten aus der Kategorie: Biowissenschaften Chemie
Der innovations-report bietet im Bereich der "Life Sciences" Berichte und Artikel über Anwendungen und wissenschaftliche Erkenntnisse der modernen Biologie, der Chemie und der Humanmedizin.
Unter anderem finden Sie Wissenswertes aus den Teilbereichen: Bakteriologie, Biochemie, Bionik, Bioinformatik, Biophysik, Biotechnologie, Genetik, Geobotanik, Humanbiologie, Meeresbiologie, Mikrobiologie, Molekularbiologie, Zellbiologie, Zoologie, Bioanorganische Chemie, Mikrochemie und Umweltchemie.
Neueste Beiträge

Bakterien für klimaneutrale Chemikalien der Zukunft
Forschende an der ETH Zürich haben Bakterien im Labor so herangezüchtet, dass sie Methanol effizient verwerten können. Jetzt lässt sich der Stoffwechsel dieser Bakterien anzapfen, um wertvolle Produkte herzustellen, die…

Batterien: Heute die Materialien von morgen modellieren
Welche Faktoren bestimmen, wie schnell sich eine Batterie laden lässt? Dieser und weiteren Fragen gehen Forschende am Karlsruher Institut für Technologie (KIT) mit computergestützten Simulationen nach. Mikrostrukturmodelle tragen dazu bei,…

Porosität von Sedimentgestein mit Neutronen untersucht
Forschung am FRM II zu geologischen Lagerstätten. Dauerhafte unterirdische Lagerung von CO2 Poren so klein wie Bakterien Porenmessung mit Neutronen auf den Nanometer genau Ob Sedimentgesteine fossile Kohlenwasserstoffe speichern können…